par Philippe Cosentino
Peu connus du grand public, les vaccins à ARN suscitent beaucoup d’inquiétudes, souvent injustifiées.
Nous proposons ici des pistes d’exploitation du logiciel Geniegen 2 utilisant les séquences du vaccin BNT162B2 (des laboratoires BioNTech-Pfizer) mais aussi de la protéine Spike naturelle du SARS CoV 2.
Ces pistes peuvent en particulier être utilisés dans le cadre du programme de spécialité de première.
Présentation rapide du vaccin
Produit par les laboratoires BioNTech-Pfizer et mis en pratique dès décembre 2020, le vaccin BNT162B2, aussi appelé Tozinaméran ou Comirnaty, contient essentiellement des molécules d’ARN messager apprêtées pour pénétrer dans les cellules (il est encapsulé dans des nanoparticules lipidiques).
Comprendre ce vaccin c’est avant tout comprendre l’information contenue sur cet ARN messager, et le produit de son expression.
Lecture de la séquence dans Geniegen 2
La séquence « complète » (brute) de l’ARN messager de ce vaccin est présente dans la banque intégrée de Geniegen2.
On peut également charger la séquence codante uniquement, ou mieux, les 2 séquences (brute et codante) à l’aide du lien direct suivant :
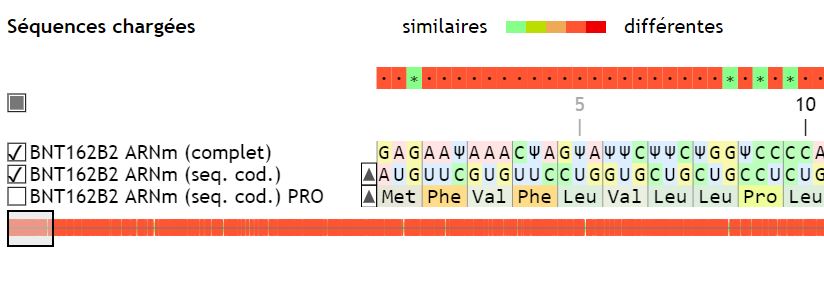
La première chose qui saute aux yeux quand on lit la séquence du vaccin dans Geniegen2, c’est la présence d’un nucléotide exotique, figuré par la lettre grecque Psi (Ψ).
Ce nucléotide est en fait de la pseudouridine. Les concepteurs du vaccin on remplacé toutes les uridines (U) de l’ARNm original par des pseudouridines (Ψ) afin de stabiliser l’ARN, et d’éviter qu’il ne soit dégradé.
La pseudouridine étant « lue » exactement comme une uridine par les ribosomes, Geniegen2 la considère comme telle et l’aligne avec les uridines.
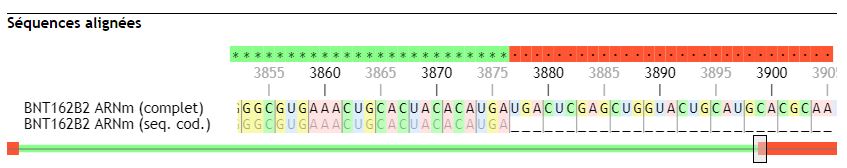
Enfin, on peut noter que la séquence « brute » de l’ARNm commence par les nucléotides GA (la guanine est méthylée) : il s’agit de la coiffe, indispensable au transport dans le cytoplasme de l’ARNm mais aussi à son expression et à sa stabilité (il protège l’ARN des exonucléases).
Alignement
Si on aligne (menu « Actions/Aligner ») cette séquence avec celle de la séquence codante (dans laquelle les Ψ sont remplacés par des U) correspondante on constate que cette dernière commence au nucléotide n°55 (par un codon AUG) et se termine par un codon stop UGA en position 3876.
En amont et en aval de cette séquence se trouvent donc des séquences qui ne seront pas traduites, mais qui pour autant jouent un rôle essentiel dans l’expression de cet ARN.
Traduction de la séquence codante
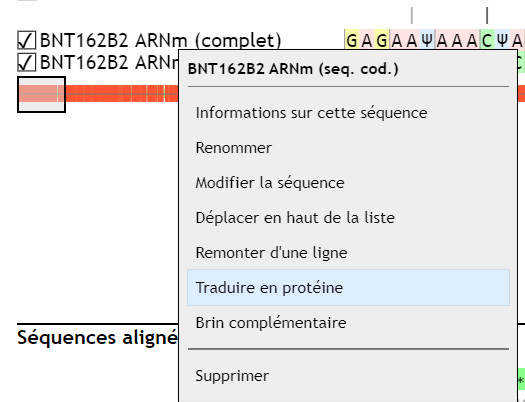
On peut traduire la séquence codante en protéine, soit en cliquant avec le bouton droit sur le titre de celle-ci (dans la moitié supérieure de l’écran), soit en ne sélectionnant que celle-ci et en passant par le menu « Actions/Traduire les séquences sélectionnées ».
On obtient alors un polypeptide de 1273 résidus (acides aminés) :
On peut alors comparer cette protéine à la protéine Spike naturelle du virus SARS-CoV 2, en allant charger cette séquence dans la banque de Geniegen 2 (Fichier / Ouvrir la banque).
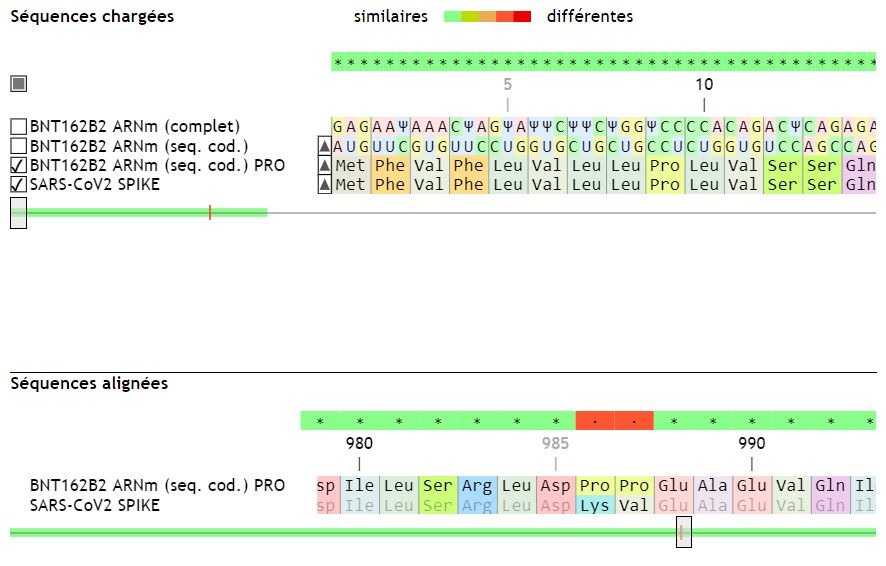
On peut alors aligner la séquence de la protéine issue de la traduction de l’ARN du vaccin avec la protéine « naturelle » du coronavirus :
On constate que les deux séquences sont identiques à l’exception des résidus n° 986 et n°987 qui sont des prolines dans la protéine issue de l’expression du vaccin.
Le produit de l’expression de ce vaccin est donc une version mutée de la protéine Spike du SARS CoV 2.
Cette double substitution introduite par les chercheurs permet à la protéine Spike « isolée » de ne pas se « recroqueviller » sur elle même, et d’avoir une conformation proche de celle qu’elle aurait « in situ » sur une particule virale (la proline est un acide aminé qui introduit de la rigidité dans la chaîne polypeptidique).
Sans cette substitution, la protéine adopterait une forme tridimensionnelle bien différente de celle que l’on souhaite (le pic « spike » présent sur les particules virales).
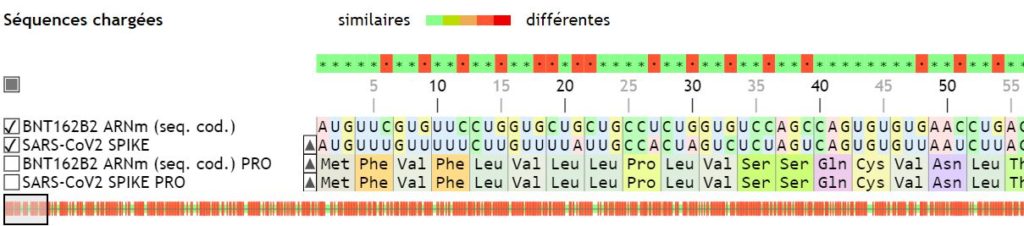
A faire remarquer : si les deux protéines (la protéine naturelle et la protéine induite par le vaccin) sont identiques à 2 acides aminés près, ce n’est pas du tout le cas des séquences nucléotidiques.
En effet, si on charge (à partir de la banque) la séquence de nucléotides du gène Spike du SARS-CoV2, et qu’on la compare à la séquence codante du vaccin, on remarque de nombreuses différences, qui cependant n’affectent pas le produit de la traduction (car ce sont des codons synonymes). Ces modifications de la séquence nucléotidiques ont été introduites par les chercheurs pour une plus grande efficacité du vaccin (ils ont remplacé par des G autant que possible pour augmenter l’efficacité de la traduction).
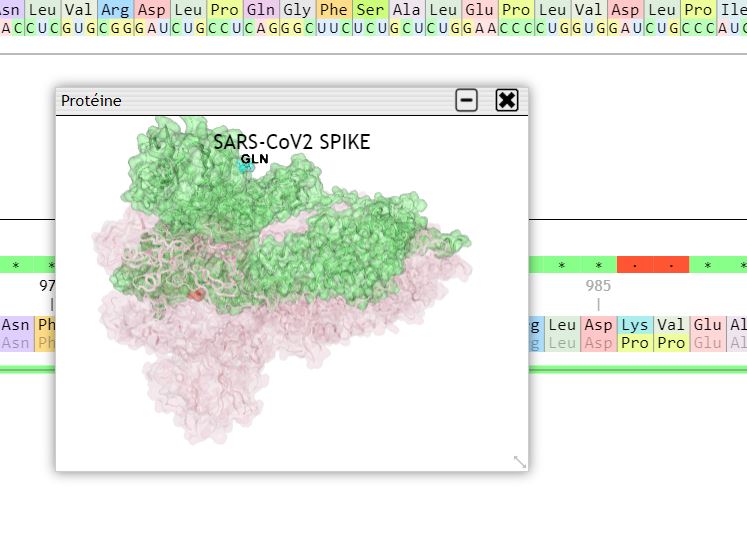
Enfin, notons que la structure 3D de la protéine (naturelle) peut être visualisée dans Geniegen2, à l’aide d’un clic droit sur le titre de celle-ci :
On peut faire remarquer aux élèves si on le souhaite, que si on compare la séquence issue de la traduction avec celle de la protéine en 3D, on constate qu’il manque des acides aminés au début de la séquence, et même au milieu de celle-ci : cela montre qu’entre le polypeptide issu de la traduction, et la protéine finale, il y a une étape de maturation (des morceaux sont retirés) tout comme avec l’ARN prémessager.
En résumé
L’étude des séquences nous ont permis de comprendre que l’expression de l’ARN contenu dans le vaccin aboutirait à une protéine mutée de forme équivalente à la protéine Spike naturellement exprimée par le virus.
Les cellules humaines ayant incorporé cet ARNm vont donc synthétiser ces protéines et les présenter au système immunitaire, ce qui va induire chez ce dernier l’activation de clones de lymphocytes spécifiques capables de neutraliser le virus, et à plus long terme d’une mémoire immunitaire dirigée contre ce dernier.
Liens
Lien direct ouvrant les séquences présentées dans cet article dans Geniegen2