par Philippe Cosentino
Pour ceux qui ne le connaissent pas encore, Geniegen2 est un logiciel gratuit qui permet de traiter des séquences nucléotidiques et polypeptidiques, et qui est destiné à l’enseignement, notamment en lycée.
Cette application propose de nombreuses fonctionnalités, et au dire de certains enseignants, cette profusion représente parfois un obstacle à leurs objectifs pédagogiques, en mâchant un peu trop le travail de leurs élèves.
Comment faire, par exemple, pour évaluer les élèves sur leur capacité (en prépa BCPST par exemple) à construire un phénogramme (arbre) de type UPGMA, vu que le logiciel leur propose de le construire automatiquement ?
Difficile donc, a priori, de contenter ceux qui souhaitent voir ces fonctionnalités disparaître du logiciel, tout en ne lésant pas ceux qui les apprécient et les utilisent.
La solution existe pourtant, et c’est ce que nous allons décrire dans cet article.
Principe général
L’objectif est de limiter l’accès à certaines fonctionnalités de Geniegen2, ou, en d’autres termes, de « brider » le logiciel.
Pour proposer aux élèves une version bridée de Geniegen2, l’enseignant devra simplement renommer le fichier de séquence, au format « Anagène » (.edi), qu’il leur fournit.
Forcer la comparaison simple (sans alignement) par défaut
Par défaut, Geniegen2 incite l’élève à aligner les séquences avant de les comparer. Un message allant dans ce sens apparaît dans la moitié inférieure de l’écran, et le menu « Action » met bien en avant la fonction « Aligner les séquences ».

Cependant, l’enseignant peut souhaiter que cette action ne soit pas la première que tente l’élève, notamment s’il compte, par exemple, étudier les conséquences des délétions, et leur montrer l’importance de l’alignement.
Il peut alors choisir de faire en sorte que la comparaison par défaut soit « sans alignement ».
Pour cela il lui suffira de renommer le fichier (si on prend l’exemple des séquences de la thalassémie) « thalassemie.edi », en « thalassemie.na.edi ».
Au chargement du fichier de séquence, Geniegen2 détecte que l’extension du fichier comporte « .na », et le mode de comparaison par défaut devient alors « Comparer sans aligner ».
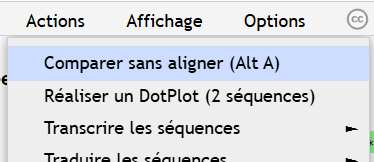
Si l’élève souhaite aligner les séquences, il devra alors le préciser dans le menu « Options / Algorithme d’alignement ».
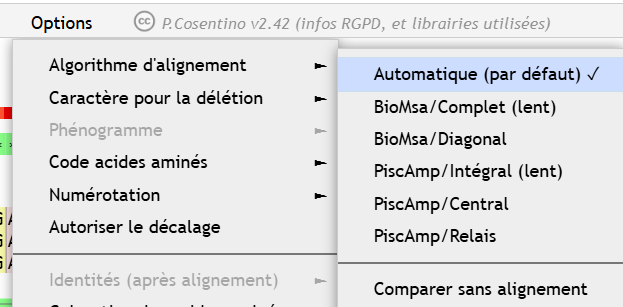
Toute cette manipulation est fastidieuse, mais normalement, il n’aura plus jamais à la refaire jusqu’à la fin de sa scolarité, étant donné qu’il n’y a aucune bonne raison (autre que celle décrite plus haut) de comparer sans aligner.
Contraindre l’élève à utiliser les fonctionnalités du logiciel pour comparer
Par défaut, Geniegen2 affiche plusieurs indicateurs visuels qui mettent en évidence les similitudes et les différences entre les séquences, et ce, dès l’affichage initial des séquences (dans la moitié supérieure de l’écran).
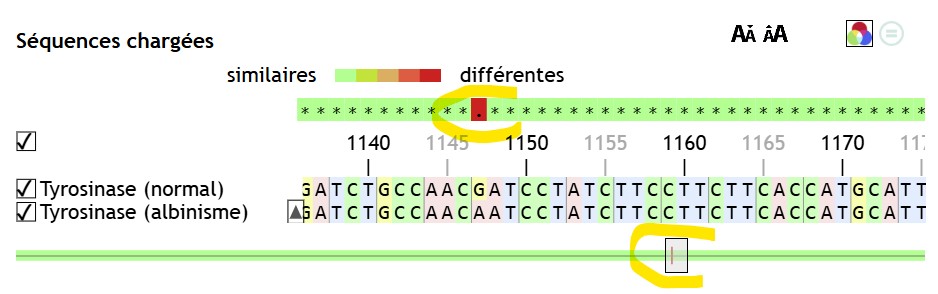
À cause de ces indices, qui ont bien entendu leur intérêt, certains élèves ne voient pas l’intérêt d’aligner les séquences (ou même de passer par les commandes du logiciel).
Il est désormais possible de désactiver tous ces indices colorés, uniquement dans la moitié supérieure de l’écran.
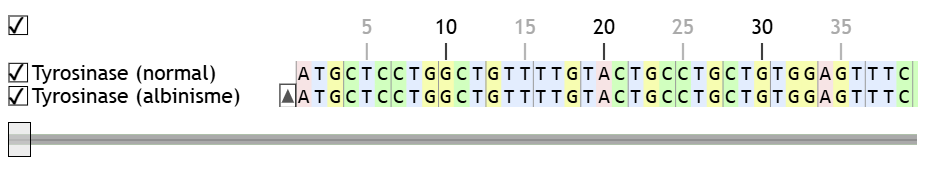
Comme on peut le constater sur la capture d’écran ci-dessus, la barre de défilement, désormais grise, ne comporte aucun marqueur indiquant une différence. De plus, les indicateurs de similarité (les astérisques et les points) ont disparu.
Après alignement (ou après comparaison simple, le cas échéant), les séquences traitées apparaissent en bas de l’écran, avec les marqueurs colorés.
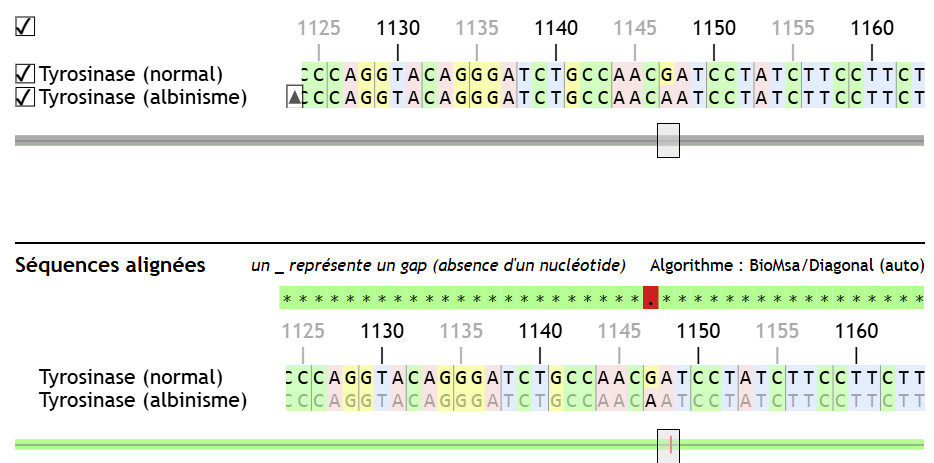
Pour arriver à ce résultat, il suffit de renommer le fichier en ajoutant .nc. dans son extension.
Par exemple : « sequences-albinisme.nc.edi »
Désactiver l’affichage des phénogrammes (arbres de similarité)
Geniegen2 propose de construire automatiquement les phénogrammes (WPGMA ou UPGMA) à l’issue d’un alignement de séquences.
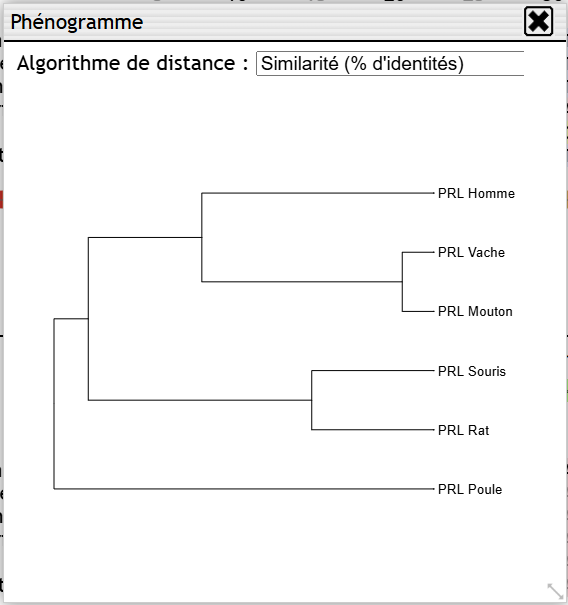
Cependant, notamment en classe préparatoire aux grandes écoles, ou à l’université, l’enseignant souhaiterait pouvoir former ou évaluer ses élèves sur leur capacité à construire, par eux-mêmes, ces arbres.
Le problème se pose également dans le cadre du concours en BCPST, où cette fonctionnalité peut poser un souci évident.
La solution est encore une fois de renommer le fichier en incluant .nt. dans l’extension.
Par exemple : « prolactines.nt.edi »
À l’ouverture du fichier de séquences ainsi renommé, la fonctionnalité qui permettait d’afficher les arbres aura tout simplement disparu du menu. Il n’y a aucun risque que l’élève la réactive, le seul moyen étant de fermer et de relancer complètement le logiciel.
Combiner les restrictions
Il est possible de combiner les différentes restrictions présentées précédemment en concaténant les extensions.
Ainsi, si l’enseignant souhaite à la fois désactiver les indices colorés et l’affichage des arbres, il lui suffit de renommer ses séquences en mettant « .nc.nt. » dans l’extension.
Par exemple : « mucoviscidose.nc.nt.edi »
Remarque : l’ordre importe peu, on peut mettre .nc.nt.edi ou .nt.nc.edi (tant que ça se termine par .edi).
Toutes les possibilités sont résumées dans le tableau ci-dessous :
| Nom de fichier | Restrictions |
| fichier.edi | Aucunes |
| fichier.nc.edi | Pas d’indices de similarité |
| fichier.na.edi | Comparaison simple par défaut |
| fichier.nt.edi | Pas de phénogramme |
| fichier.nc.na.edi | Pas d’indices de similarité et comparaison simple par défaut |
| fichier.nc.nt.edi | Pas d’indices de similarité et pas de phénogramme |
| fichier.na.nt.edi | Comparaison simple par défaut et pas de phénogramme |
| fichier.nc.na.nt.edi | Toutes les restrictions ci-dessus combinées |
Que faire si l’enseignant travaille à partir des séquences de la base ?
La procédure que nous avons décrit repose sur le renommage d’un fichier de séquence.
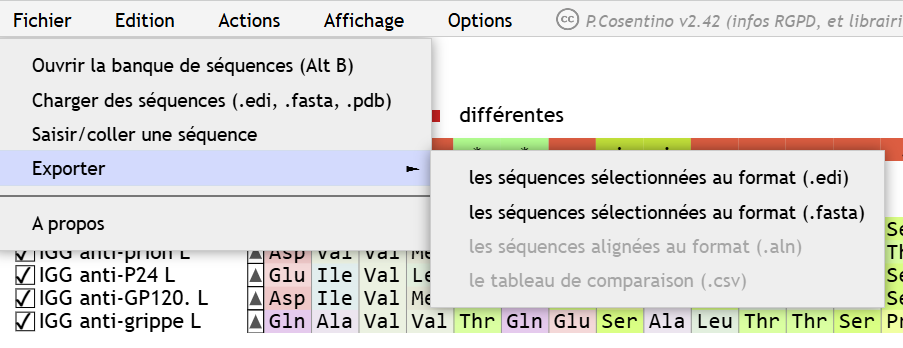
Si l’enseignant compte donner à ses élèves des séquences présentes dans la banque interne de Geniegen2, il lui suffira de réaliser cette manipulation en amont :
- Charger les séquences souhaitées à partir de la banque
- Les exporter (via le menu « Fichier/Exporter ») au format .edi
- Renommer le fichier obtenu avec les extensions adéquats
- Fournir ce fichier aux élèves
Conclusion
On pourrait voir dans ces manipulations une simple astuce technique, mais la question de fond est ailleurs.
Que cherche-t-on réellement à évaluer ? La capacité des élèves à utiliser un logiciel, ou leur compréhension des méthodes et des raisonnements sous-jacents ?
En permettant de masquer certaines fonctionnalités, Geniegen2 cesse d’être un outil qui fait à la place de l’élève, pour redevenir un support d’apprentissage adaptable aux objectifs de l’enseignant.
Reste une question, qui n’est pas entièrement confortable : jusqu’où faut-il guider, et à partir de quand faut-il laisser faire ?
Ces options ne donnent pas une réponse unique, mais elles offrent au moins la possibilité de choisir.
Liens
Lien vers l’application Geniegen2 en ligne sur le site pédagogique de Nice
Lien miroir vers l’application Geniegen2 en ligne sur le site de l’auteur (CosPhiLog)
Lien pour télécharger la version exécutable de Geniegen2

